一项大规模群体宏基因组研究对反刍动物胃肠道病毒群落进行了系统梳理。研究团队由中国科学院亚热带农业研究所谭志良教授领衔,相关成果于1月6日发表于《高级研究杂志》。
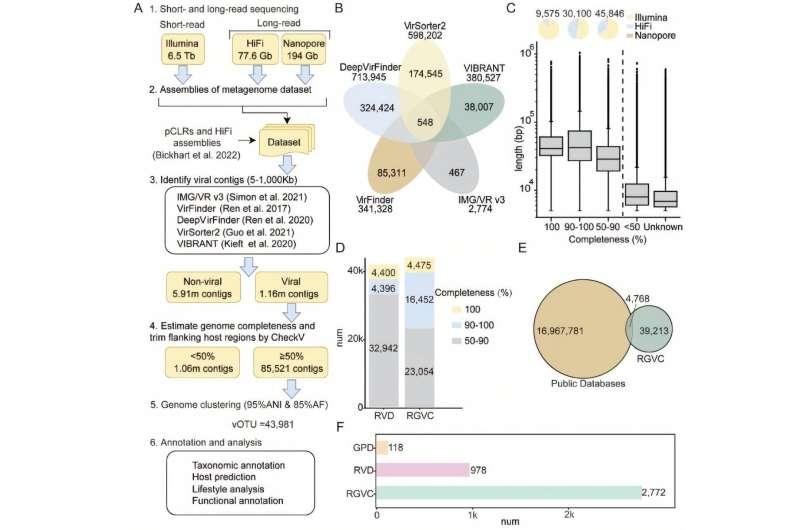
研究人员整合了来自七种反刍动物、覆盖10个胃肠道区域的373个宏基因组样本,构建反刍动物胃肠道病毒组目录(RGVC)。研究结合短读与长读测序数据,鉴定出近44,000个病毒操作分类单元(vOTUs),其中89.3%为此前未被记录的病毒序列,从而扩展了对反刍动物病毒多样性的认识。
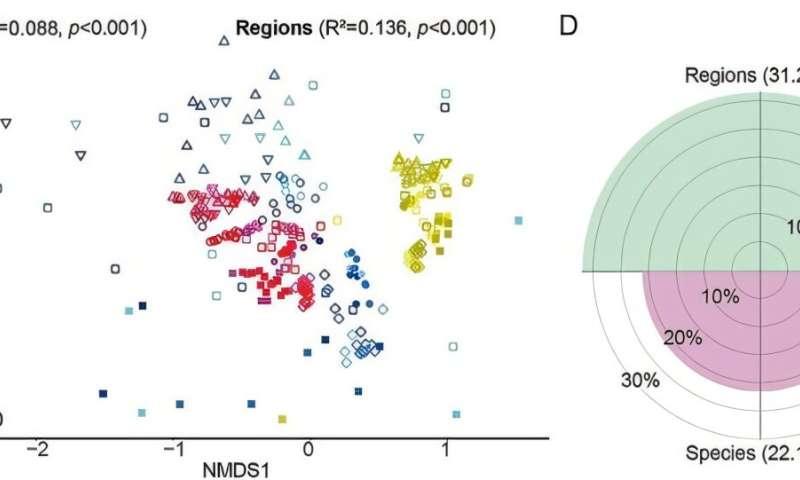
研究显示,反刍动物胃肠道病毒群落具有明显的空间异质性。病毒组成的差异主要与胃肠道生理区域相关,例如胃、小肠和大肠等区段,而不是由宿主反刍动物物种本身所主导。研究同时指出,这种区域性分布与推测的微生物宿主分布密切相关。
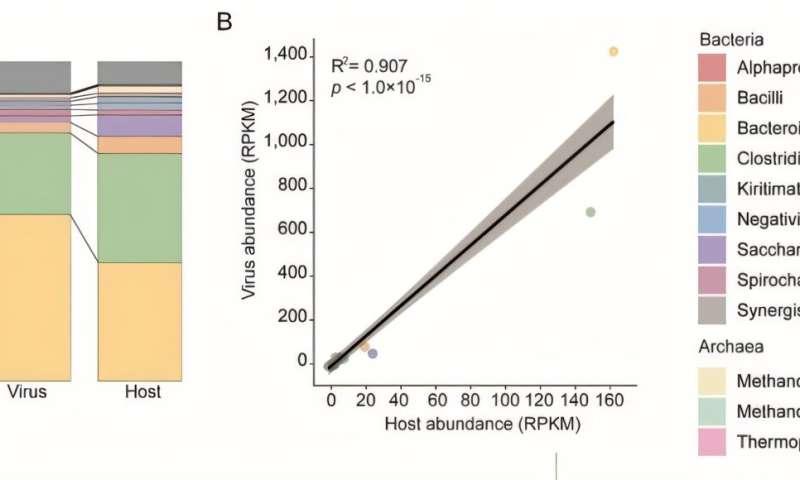
在生物信息学分析中,研究团队识别出超过10,000个高置信度病毒—宿主配对关系,涉及4,600多个原核宿主与近6,000个病毒。结果显示,病毒丰度与其对应宿主的丰度呈强相关,提示局部原核生物群落差异可能是驱动病毒空间分布的重要因素。

研究还发现,近一半病毒采用溶原生活方式,即将其DNA整合进宿主基因组以实现长期存活,并且该生存策略的优势沿消化道呈系统性变化。
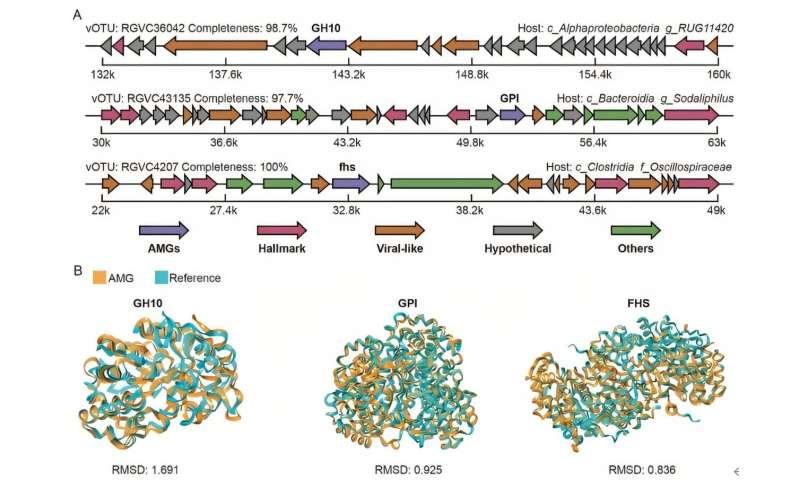
此外,研究在多种病毒基因组中检测到与关键代谢过程相关的辅助代谢基因(AMGs),涵盖碳水化合物代谢与能量代谢等功能。研究指出,这些AMGs在不同胃肠道区域的分布存在差异,反映其在局部代谢功能上的特征。通过基因组分析与三维蛋白质建模,研究进一步确认了部分关键AMGs的病毒来源及其功能活性。
共同通讯作者王敏教授表示,这是一次从空间生态学视角对反刍动物胃肠道病毒进行系统探索的研究,相关结果有助于理解病毒的分布、生存策略及功能影响,并为在特定胃肠道区室内开展病毒—宿主相互作用的精准调控提供可能。











