研究组织与器官形态被认为是理解其形成过程的重要环节。由于胚胎发育在三维空间中进行,研究人员在使用二维图像与方法描述三维过程时往往面临局限。为此,EMBL巴塞罗那的研究团队开发了LimbLab——一套用于生长肢芽三维可视化与分析的开源流程。
面向三维肢体发育研究的专用平台
LimbLab主要用于小鼠肢体发育研究,但研究团队表示,其工作思路也可为处理复杂体积成像数据的研究人员提供参考。相关方法已在《BMC生物信息学》发表。
该研究第一作者、EMBL Sharpe小组博士生Laura Aviñó-Esteban表示,团队开发LimbLab的原因在于现有工具忽视了胚胎发育的一些关键方面,且并非专为发育生物学研究设计。
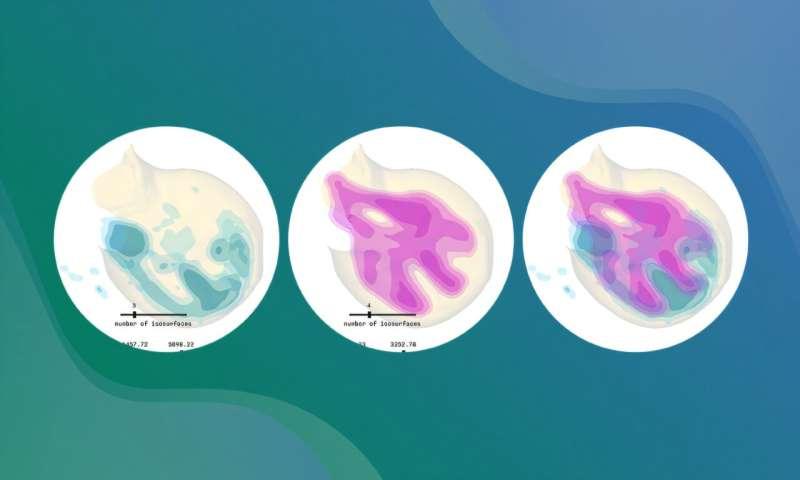
在肢体发育研究中,研究人员常需要特定的软件能力,例如依据样本可见特征为其分配发育年龄,或对样本图像进行对齐与形态变换,以便开展准确且一致的比较。二维领域已有eMOSS、LimbNET等工具,但在三维分析方面缺乏对应方案。LimbLab旨在填补这一空白,并支持基因表达模式的三维可视化。
LimbLab采用模块化工作流程,并在Vedo中实现。Vedo是Sharpe实验室开发的开源Python库,用于三维分析以及网格与体积渲染。
工作流程:从体积数据到对齐与展示
按照研究团队描述,LimbLab首先对显微镜获得的原始体积数据进行清理,去除噪声与伪影;随后提取组织表面信息,并构建用于计算的“网格”结构,以提升处理效率。
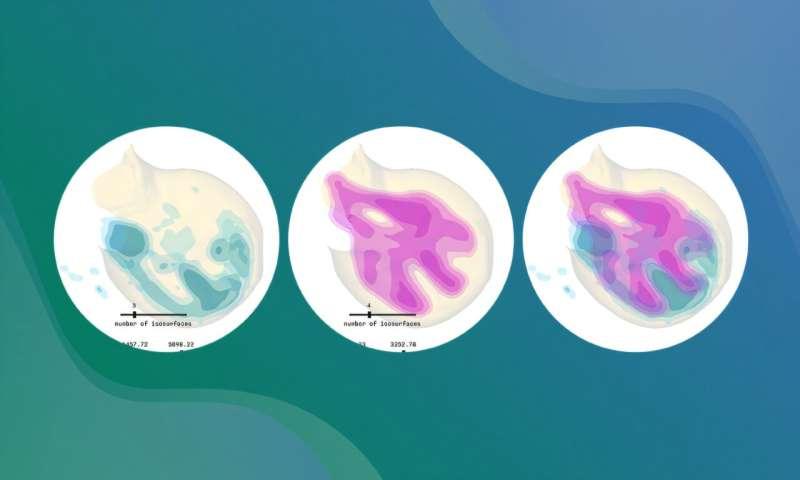
在此基础上,流程会分析样本以确定其发育年龄,并将样本与参考模型进行对齐或形态变换。LimbLab还提供可视化方法,帮助研究人员在完整三维空间中探索与展示基因表达。流程各步骤配有日志记录与标准化处理,以提高可重复性。
应用范围延伸至类器官、肿瘤等三维成像研究
研究团队指出,该流程的意义不局限于肢体发育。类器官、肿瘤以及工程组织等研究同样依赖三维体积成像数据。LimbLab展示了专用流程如何将复杂的三维数据整理为更清晰、可对齐的结果。
研究人员同时强调成像研究中的可重复性问题,认为处理过程中的细微差异可能带来不同的生物学解释。LimbLab被视为一项概念验证,展示专用计算工具在三维生物数据分析中的作用。
LimbLab以开源方式发布,研究团队称其易于安装并提供完整文档。尽管当前版本针对小鼠肢芽进行了优化,团队计划将其适配至其他物种与组织,以支持更广泛的研究需求。











