染色体由长链DNA折叠形成紧凑结构,在维持基因组关键区域可及性的同时,将不常用部分相对“隐藏”。由于染色体体系规模庞大,其结构与动态特征的解析长期依赖实验数据与理论方法的结合。
赖斯大学José Onuchic与Vinícius Contessoto在近期论文中介绍了一种名为FI-Chrom的方法,旨在基于真实数据构建染色体三维图谱。相关研究发表于《美国国家科学院院刊》(Proceedings of the National Academy of Sciences)。
研究团队表示,FI-Chrom以染色体Hi-C图谱数据为基础。Hi-C图谱将染色体划分为长度单位“珠”,并记录不同“珠”之间接近的频率。该类数据反映的是任意两段序列相邻的概率关系,本身并不直接提供三维空间坐标。
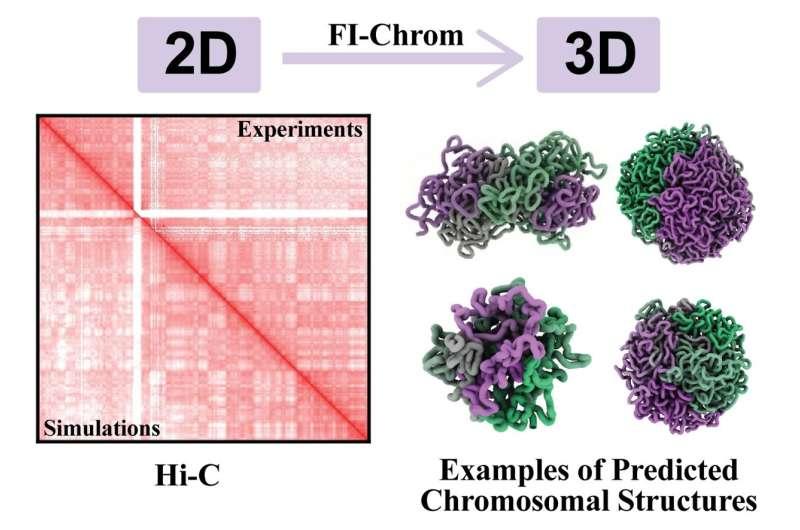
研究人员将这一问题类比为在既定约束下的“逻辑谜题”:例如某一“珠”与其他“珠”分别以不同概率接近。理论上,只要为每个“珠”找到不违背Hi-C约束的空间位置,就能构建三维模型;但实际数据规模巨大,Hi-C图谱可能包含数十万个“珠”以及数千万条接触映射关系,使得求解难度显著增加。
Onuchic在论文中称,研究团队开发了开放获取程序FI-Chrom,用于将Hi-C图谱转化为染色体三维模型。论文第一作者、博士后Antonio Oliveira Jr采用逆统计力学方法构建了该程序。
Contessoto表示,FI-Chrom对研究人员开放使用,预期可用于从人类、酵母到细菌等多种生物体的染色体结构研究。
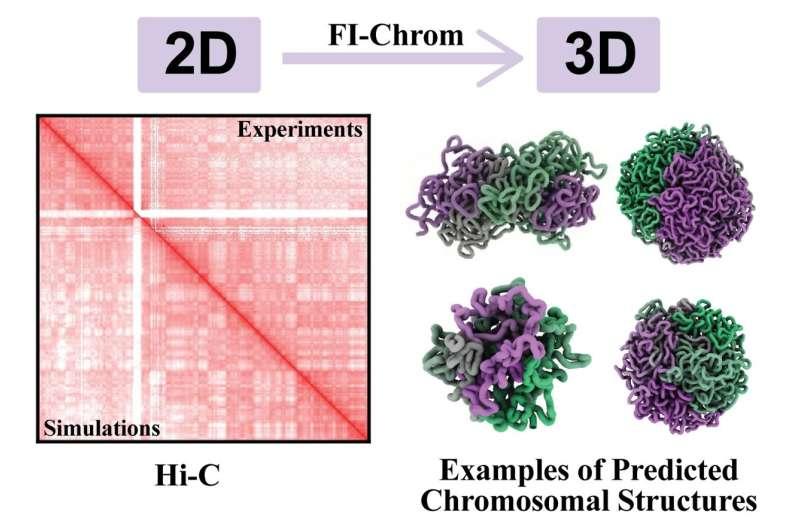
研究团队介绍,Oliveira在最大熵框架下对模型进行训练,并未预先向程序设定染色体应呈现的具体形态,而是让FI-Chrom在训练过程中逐步生成与已知Hi-C接触图匹配的结构集合。Oliveira称,在多轮训练后,程序生成的三维模型呈现出一些特征,这些特征无法直接从Hi-C二维图谱中观察,但在预测得到的三维结构集合中更为清晰。
除结构重建外,FI-Chrom还被用于将Hi-C数据集转化为对动态机制的刻画。研究团队指出,尽管Hi-C数据主要提供结构层面的信息,但由于其反映了不同“珠”彼此接近或远离的频率,研究人员可据此在模型不同位置推断可能的运动特征。
Contessoto同时强调,二维Hi-C图谱来自细胞群体测量,并不对应单一染色体构象,而是反映一组结构的集合。Onuchic表示,研究团队利用这些信息模拟染色质环,并通过FI-Chrom模型显示这些环为瞬时形成,而非染色体的静态特征。











